转录组测序(RNA-Seq)的研究对象是特定细胞在某一功能状态下所能转录出来的所有mRNA的总和。新一代高通量测序技术能够全面快速的获得某一物种特定组织或器官在某一状态下的几乎所有转录本序列信息,从而准确地分析基因表达差异、基因结构变异、筛选分子标记(SNPs或SSR)等生命科学重要问题。
服 务 优 势
♕ 无便向性,适用于各类型样本;
♕ 不局限于模式物种,可研究非模式物种,针对不同平台的数据,制定多套定制化流程;
♕ 整合多个转录组相关数据库,从本质上提高后期分析的广度和精度;
♕ 个性化定制分析,让您的文章脱颖而出。
单细胞转录组测序;
全转录组测序;
mRNA测序;
microRNA测序;
lncRNA测序;
circRNA测序;
RNA相对表达量qPCR检测。
服 务 流 程

客户样本:total RNA≥1.0μg(人或小鼠≥100ng);
文库构建、上机测序:6Gb、8Gb、10Gb、12Gb clean data;
数据过滤、质控:过滤掉低质量的reads、过滤掉含接头的reads、过滤掉含n多的reads;
参考基因组比对:与参考基因组进行Mapping,既可研究已知基因,亦能发掘新基因。

测序深度:
PE 150
服务周期:
15~22个工作日
| 基因结构水平分析 | 基因表达水平分析 |
| 与参考基因组比对 | 基因表达水平分析 |
| 新转录本预测 | 差异基因分析 |
| 可变剪切分析 | GO/KEGG富集分析 |
| SNP分析 | 蛋白互作网络分析 |
| InDel分析 | 转录因子注释 |
数据质控
测序得到的原始测序序列(Sequenced Reads)或者 raw reads,里面含有带接头的、低质量的reads,为了保证信息分析质量,必须对raw reads过滤,得到clean reads,后续分析都基于clean reads。在测序过程中会存在一定的错误率,测序错误率分布检查可以反映测序数据的质量。

参考序列比对
将比对到基因组上的reads分布情况进行统计,定位区域分为Exon(外显子)、Intron(内含子)
和Intergenic(基因间区)。reads与参考基因组比对率,指比对到参考基因组上的reads数目除以有效测序数据的reads数据,可反映样本的基因组拼接注释水平。

差异基因表达分析
差异表达基因以火山图、聚类热图、韦恩图等形式展示,可直观展示样本间差异基因表达的情况。用火山图可直观展示不同实验条件下差异基因的分布情况,对于有生物学重复的实验,由于DESeq已经进行了生物学变异的消除,我们对差异基因筛选的标准一般为:padj<0.05。对于无生物学重复实验,我们采用degseq软件,筛选差异基因时设定更为严格的阈值 log2="" fold="">1且 padj < 0.005。为了增强数据的可靠度,我们建议设置生物学重复。

RNA-seq相关性分析
差异基因表达分析
差异表达基因以火山图、聚类热图、韦恩图等形式展示,可直观展示样本间差异基因表达的情况。用火山图可直观展示不同实验条件下差异基因的分布情况,对于有生物学重复的实验,由于DESeq已经进行了生物学变异的消除,我们对差异基因筛选的标准一般为:padj<0.05。对于无生物学重复实验,我们采用degseq软件,筛选差异基因时设定更为严格的阈值 log2="" fold="">1且 padj < 0.005。为了增强数据的可靠度,我们建议设置生物学重复。
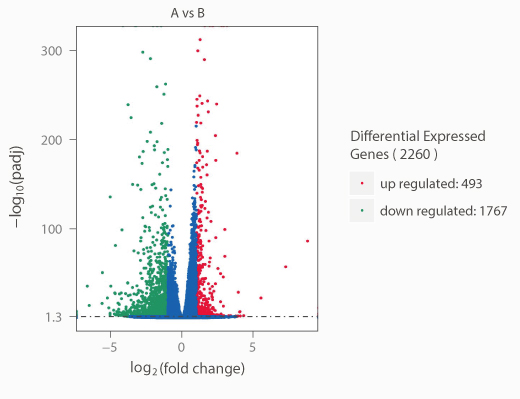
差异基因表达筛选及聚类分析
差异基因GO富集分析
差异基因GO富集柱状图,直观的反映出在生物过程(biological process)、细胞组分(cellular component)和分子功能(molecular function),富集的GO term上差异基因的个数分布情况。
可挖掘差异基因的功能及所在的信号通路,缩小基因筛选的范围。

典 型 案 例
水稻根系响应氧化石墨烯纳米片的应激反应与恢复模式
Systemic Stress and Recovery Patterns of Rice Roots in Response to Graphene Oxide Nanosheets
期刊:Environmental Science & Technology
影响因子:5.393
发表单位:南开大学
发表时间:2017.02
氧化石墨烯(GO)是一种 2D 工程材料,已经被广泛应用于各个领域,包括生物学、医学、化学、环境保护。大部分纳米材料在使用过程中被释放到环境中,因此,纳米材料潜在的环境风 险已引起越来越多的关注。研究表明,0.1−10 mg/L 的 GO 可诱导绿色藻类细胞结构损伤、氧化作用和代谢紊乱;5−500 mg/L 的 GO 将抑制水稻生长。目前,大多数研究都仅限于对 纳米颗粒的生物应激反应,而应激恢复相关的信息在很大程度上是未知的。
研究过程

1. 水稻根系的应激与恢复模式
KEGG 富集分析表明,S1 组下调表达的基因主要富集在苯丙氨酸代谢 和苯丙素的生物合成途径等代谢通路中。S2 组上调基因参与到次生代 谢和二萜类化合物的生物合成途径中。该结果表明,处理后的恢复过 程增强了水稻抗性(图1b)。蛋白互作网络分析表明,GO 处理组中下调 表达的基因与苯丙氨酸、次生代谢相关;上调表达基因与次生代谢相关 (图1d)。因此,GO 处理可促进次生代谢。苯丙氨酸代谢、次生代谢途 径的改变,过氧化物酶相关的差异表达基因,均参与了水稻根系响应 GO 的应激反应与恢复机制。
2. GO降低根系的吸收能力
TIP1−2 等水通道蛋白相关基因在 S1 组中下调表达,在 S2 组中恢复到对照组水平,这一结果与 GO 降低水稻根 系水吸收能力的结果一致。蛋白互作分析表明,硼转运 蛋白、海藻糖-6-磷酸合成酶基因的下调表达,与水通道 蛋白相关基因下调表达相关。
3. 根系吸收 GO 引起的氧化胁迫
生理实验表明,S1 组水稻侧根生长受到抑制,S2 组 水稻根系数量恢复到正常水平。同时,编码侧根蛋白 1 的 基因(OS06G0712600)下调表达,抑制侧根生长 的色氨酸合成酶β链编码基因上调表达,萌发素类蛋 白编码 (GER6)等促进主根生长的基因上调表达。

本研究结果表明GO影响了水稻表达谱,进而影响了氧化胁迫、根系发育、细胞壁合成、激素代谢过程。水稻根系对GO处理的响应和适应过程是通过苯丙氨酸代谢、次级代谢、激素代 谢、过氧化物酶活性调节等因素共同实现的。本实验研究了纳米材料对植物生长发育的影响,揭示了植物对纳米材料适应性的分子机制,对纳米材料的安全性评估具有重大意义。
QX Zhou, HG Hu, et al. Systemic Stress and Recovery Patterns of Rice Roots in Response to Graphene Oxide Nanosheets. Environmental Science & Technology , 2017.








